性别:男
电子邮件: renjian@sysucc.org.cn
导师类型: 博士生导师
实验室主页: https://www.renlab.cn/
职称: 教授
学历: 博士
学科方向
0710Z1-生物信息学
0860-生物与医药
研究方向
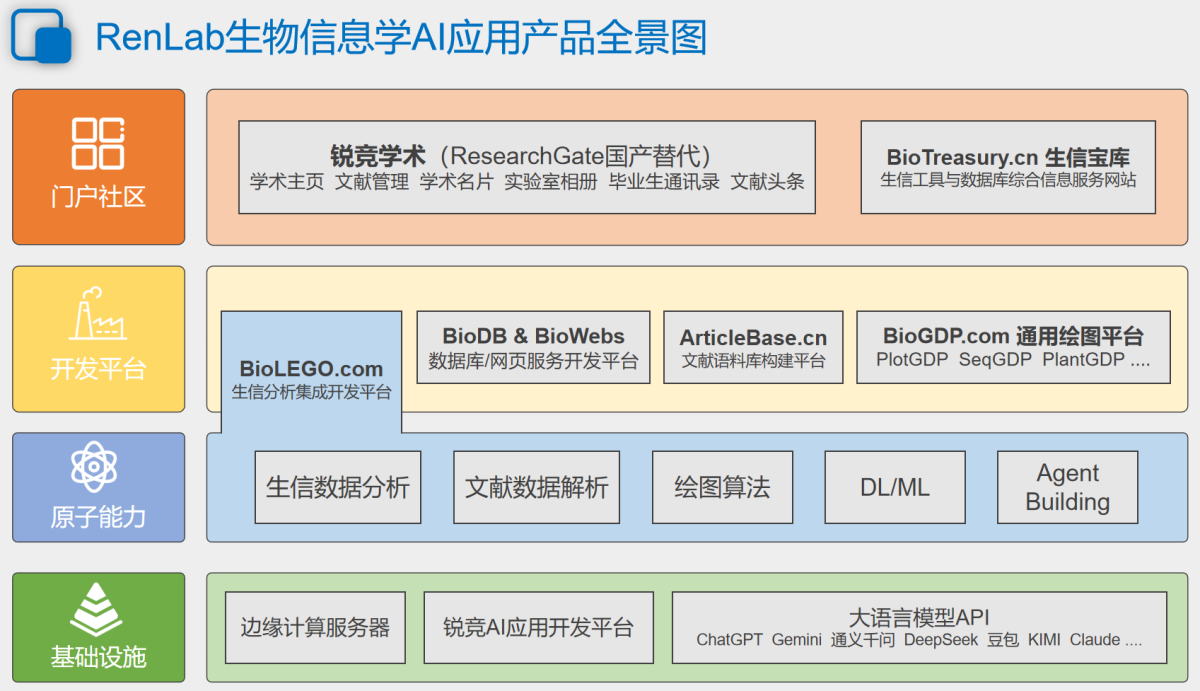
实验室主要致力于基于AI技术打造生物信息学基础开发平台,为生信领域提供科研与教学整体解决方案。此外还有生物大分子修饰(蛋白质翻译后修饰与RNA修饰)预测算法、肿瘤多组学数据分析、生物类数据库与工具软件开发等多个研究分支。
个人经历
1998至2002年就读于上海交通大学动力与能源工程学院,获核工程与核技术专业学士学位。2002至2007年在中国科学技术大学近代物理系金革教授实验室攻读博士期间参与国家大科学工程项目"大天区面积多目标光纤光谱望远镜"(LAMOST),并承担其中的巡天战略系统的研发工作,在计算机算法和大型工程软件设计开发方面具有丰富的经验。2007年7月获得物理电子学工学博士学位之后进入中国科学技术大学生命科学学院温龙平研究组进行博士后研究工作,将计算机和天文学算法以及工程学思想成功运用到生物信息学领域,开发了数十款生物信息学工具与数据库。2010 年3月获中山大学生命科学学院“百人计划”引进,2011年12月晋升教授。
1998.09 – 2002.07 学士 上海交通大学动力与能源工程学院核工程与自动化专业
2002.09 – 2007.06 博士 中国科学技术大学近代物理系物理电子学专业
2007.07 – 2010.03 博士后 中国科学技术大学生命科学学院
2010.03 – 2011.12 副教授 中山大学生命科学学院
2011.12 – 今 教授 中山大学生命科学学院
2014.07– 今 教授(双聘) 中山大学肿瘤防治中心
讲授课程
《生物信息学》,《生产实习》
学术成就
进入生物领域后,在包括Nucleic Acids Research(18篇), Cell Research(2篇), Cancer Research, Bioinformatics等国际著名杂志上发表SCI 论文70余篇(32篇IF>10.0),其中通讯或一作40篇,累计影响因子740,ESI高被引论文6篇,相关文章被引用10000余次,H-index 46。主持国家自然科学基金6项,作为骨干参与科技部项目4项。发布生物信息学工具及数据库30多个,获颁软件著作权登记证书15项。
在产业化方面,2016年创立锐竞科研采购平台(https://www.rjmart.cn),并担任广州锐竞信息科技有限责任公司CEO。锐竞平台已有来自全国的3万多家供应商入驻,上线了1.8亿种科研试剂耗材及各类服务,目前已经是全国最大的科研电商平台,500多家高校与医院已经使用该平台采购了200亿元的科研用品。有效地降低了科研采购成本,同时把科研人员从“报销繁”中解脱出来。锐竞也构建了新型科研信息化基础平台,助力科研机构数字化转型,积极参与“数字中国”建设。锐竞公司2021年入选未来医疗100强,德勤中国高科技高成长50强。2022年入选广东省专精特新企业与广州市硬科技百强企业。2023年入选广州市“隐形冠军”企业、广州“未来独角兽”创新企业、广州拟上市“领头羊”50强企业。2024年获第十三届中国创新创业大赛广州市一等奖(第一名),广东省二等奖。
人才培养
实验室已培养40余名硕士博士,其中4位获聘教授:左志向(中山肿瘤)、赵齐(中山肿瘤)、蒋帅(河南医科院)、苗彦彦(河南医科院),以及6位副教授:谢宇斌(中山一院)、郑悦媛(中山七院)、罗晓彤(中山六院)、刘文忠(四川轻化工大学)、李慧勤(河南医科院)、张印(河南医科院)。十多名毕业生就职于华为、腾讯、阿里巴巴、拼多多、美团、希音、百济神州、百度、锐竞等企业。
承担课题
- 国家自然科学基金面上项目,32470709,m6A修饰调控肿瘤细胞化疗敏感性的计算分析与机制研究,2025/01-2028/12,50万,在研,主持
- 国家自然科学基金重大研究计划培育项目,91753137,基于深度学习算法的生物大分子修饰分析平台的构建及应用,2018/01-2020/12,70万,结题,主持。
- 国家自然科学基金面上项目,31771462,单碱基精度RNA甲基化修饰组学数据分析工具构建及应用,2018/01-2021/12,60万,结题,主持。
- 广州市健康医疗协同创新重大专项,201604020003,鼻咽癌和结直肠癌生物医学大数据平台建设及精准医疗应用研究,2016/01-2018/12,154.2/600万,结题,参与。
- 广州市健康医疗协同创新重大专项,201604046001,医学外显子组高通量检测产业化规模应用关键问题研究,2016/05-2019/04,80/800万,结题,参与。
- “广东特支计划” 科技创新青年拔尖人才,2014TQ01R387,2015/04-2018/03,30万,结题,主持。
- 国家自然科学基金面上项目,31471252,基于双分子荧光互补技术的小类泛素修饰因子调控机制的系统研究,2015/01-2018/12,85万,结题,主持。
- 国家国际科技合作专项,2014DFB30020,中国人类蛋白质组学数据的知识发现,2014/04 -2018/04,200/2857万,已结题,子课题负责人。
- 教育部重大科技基础培育计划,基于“天河二号”超级计算机的肿瘤多组学数据分析平台构建,2016/05-2017/05,40万,结题,主持。
- 教育部新世纪优秀人才,NCET-13-0610,2014/01-2016/12,50万,已结题,主持。
- 广东省自然科学杰出青年基金(省杰青,首批16人),S20120011335,蛋白质翻译后修饰相关算法及工具设计,2012/10-2016/10,100万,已结题,主持。
- 广州市珠江科技新星(市人才计划,首批),2011J2200042,蛋白质翻译后修饰计算分析平台构建,2011/11-2014/10,30万,已结题,主持。
- 国家自然科学基金面上项目,31071154,蛋白质翻译后修饰受可变剪切影响的系统生物学研究,2011/01-2013/12,40万,已结题,主持。
- 国家自然科学基金青年基金,30900835,蛋白质共价修饰相关序列模体的计算发现,2010/01-2012/12,20万,已结题,主持。
论文专著
- JiangS , LiHQ , ZhangLWY ,MuWP, ZhangY, ChenTJ, WuJX, TangHY, ZhengSX, LiuYF, WuYX, LuoXT, XieYB*, RenJ*.Generic Diagramming Platform (GDP): a comprehensive database of high-quality biomedical graphics.Nucleic Acids Research. 2025;53(D1):D1670-D1676(IF:13.1, cited by 852,ESIHotPaper)
- Ren J, Wen LP, Gao XJ, Jin CJ, Xue Y, Yao XB. DOG 1.0: illustrator of protein domain structures.Cell Research. 2009;19(2):271-273. (IF:25.9, cited by 582)
- XieYB, LiHQ, LuoXT, LiHY, GaoQY, ZhangLWY, TengYY, ZhaoQ, ZuoZX, RenJ*. IBS 2.0: an upgraded illustrator for the visualization of biological sequences.Nucleic Acids Research. 2022;50(W1):W420–426(IF:13.1,cited by 200)
- Zhao Q, Xie YB, Zheng YY, Jiang S, Liu WZ, Mu WP, Liu ZX, Zhao Y, Xue Y* and Ren J*.GPS-SUMO: a tool for the prediction of sumoylation sites and SUMO-interaction motifs.Nucleic Acids Research. 2014;42(W1): W325-330. (IF:13.1, cited by 496,ESIHCP)
- Liu WZ, Xie YB, Ma JY, Luo XT, Nie P, Zuo ZX, Lahrmann U, Zhao Q, Zheng YY, Zhao Y, Xue Y* and Ren J*.IBS: an illustrator for the presentation and visualization of biological sequences.Bioinformatics. 2015;31(20):3359-3361(IF:5.4, cited by 929,ESIHotPaper)
- Zheng YY, Nie P, Peng D, He ZH, Liu MN, Xie YB, Miao YY, Zuo ZX* and Ren J*. m6AVar: a database of functional variants involved in m6A modification. Nucleic Acids Research. 2018; 46(D1): D139-145 (IF:13.1cited by 191)
- Zhao Q, Zhou X, Wu JX, Cai JY, Bao XQ, Tang L, Wang CY, Liu CL, Wang YK, Teng YY, Zheng MH, Mu WP, Zuo ZX, Xie YB, Luo XT* and Ren J*.BioTreasury: a community-based repository enabling indexing and rating of bioinformatics tools. Science China-Life Sciences.2024.2(67):221-229 (IF:9.5)
- Zuo ZX, Hu HJ, Xu QX, Luo XT, Peng D, Zhu KY, Zhao Q*, Xie YB*, Ren J*. BBCancer: an expression atlas of blood-based biomarkers in the early diagnosis of cancers. Nucleic Acids Research. 2020;48(D1):D789-796(IF:13.1,cited by 63)
- Ren J, Wen LP, Gao XJ, Jin CJ, Xue Y, Yao XB. CSS-Palm 2.0: an updated software for palmitoylation sites prediction. Protein Eng Des Sel. 2008;21(11):639-644.(cited by526,ESIHCP)
- Xue Y#, Ren J#, Gao XJ, Jin CJ, Wen LP, Yao XB. GPS 2.0, a tool to predict kinase-specific phosphorylation sites in hierarchy. Molecular & Cellular Proteomics. 2008;7(9):1598-1608. ( IF:4.828, cited by 605)
- Jin SH, Zhang XY, Miao YY, Liang PP, Zhu KY, She YC, Wu YX, Liu DA, Huang JJ, Ren J* and Cui J*. m6A RNA modification controls autophagy through upregulating ULK1 protein abundance. Cell Research. 2018;28:955-957 (IF:25.9, cited by 141)
- Zheng YY, Xu QX, Liu MN, Hu HJ, Xie YB, Zuo ZX*, Ren J*. lnCAR: a comprehensive resource for lncRNAs from Cancer Arrays. Cancer Research. 2019.79(8):2076-2083 (IF:8.378, cited by 51)
- Ren J, Gao XJ, Jin CJ, Zhu M, Wang XW, Shaw A, Wen LP, Yao XB, Xue Y. Systematic study of protein sumoylation: Development of a site-specific predictor of SUMOsp 2.0. Proteomics. 2009;9(12):3409-3412. (IF:3.106, cited by204)
- LuoXT, HuangYT, LiHQ, LuoYH, ZuoZX*, RenJ*, XieYB*. SPENCER: a comprehensive database for small peptides encoded by noncoding RNAs in cancer patients. Nucleic Acids Research.2022;50(D1):D1373-1381.
- HeYX, BaoXQ, ChenTJ, JiangQ, ZhangLWY, HeLN, ZhengJ, ZhaoA*, RenJ*, ZuoZX*. RPS 2.0: an updated database of RNAs involved in liquid–liquid phase separation. Nucleic Acids Research.2025;53(D1):D299-D309.
- HuangYT, ZhangLWY, MuWP, ZhengMH, BaoXQ, LiHQ, LuoXT, RenJ*, ZuoZX*. RMVar 2.0: an updated database of functional variants in RNA modifications. Nucleic Acids Research.2025;53(D1):D275-D283.
- LiuMN, LiHQ, LuoXT, CaiJY, ChenTJ, XieYB*, RenJ*, ZuoZX*. RPS: a comprehensive database of RNAs involved in liquid–liquid phase separation.Nucleic Acids Research.2022;50(D1):D347-355.
- ChenL, ChenTJ, ZhangY, LinHC, WangRH, WangYH, LiHY, ZuoZX*, RenJ*, XieYB*. TIRSF: a web server for screening gene signatures to predict Tumor immunotherapy response Nucleic Acids Research.2022;50(W1):W761-767.
- BaoXQ, ZhangY, LiHQ, TengYY, MaLX, ChenZH, LuoXT,ZhengJ, ZhaoA*, RenJ*, ZuoZX*. RM2Target: a comprehensive database for targets of writers, erasers and readers of RNA modifications. Nucleic Acids Research.2023;51(D1):D269-279.
- Xue Y*, Liu ZX, Gao XJ, Jin CJ, Wen LP, Yao XB, Ren J*. GPS-SNO: Computational Prediction of Protein S-Nitrosylation Sites with a Modified GPS Algorithm. Plos One. 2010;5(6): e11290. (cited by192)
- Xue Y*, Liu ZX, Cao J, Ma Q, Gao X, Wang QQ, Jin CJ, Zhou YH, Wen LP, Ren J*. GPS 2.1: enhanced prediction of kinase-specific phosphorylation sites with an algorithm of motif length selection. Protein Eng Des Sel. 2011;24(3):255-260. (cited by 205)
- Zhang Y, Xie YB, Liu WZ, Deng WK, Peng Di, Wang CW, Xu HD, Ruan C, Deng YJ, Guo YP, Lu CJ, Yi C, Ren J* & Xue Y*. DeepPhagy: a deep learning framework for quantitatively measuring autophagy activity in Saccharomyces cerevisiae. Autophagy. 2020;16(4):626-640(IF:11.059, cited by 2)
- Luo XT, Li HQ, Liang JQ, Zhao Q, Xie YB*, Ren J* and Zuo ZX*. RMVar: an updated database of functional variantsinvolved in RNA modifications. Nucleic Acids Research. 2021;49(D1):D1405-1412. (IF: 14.9,cited by 171, ESIHCP)
- Ren J, Jiang CH, Gao XJ, Liu ZX, Yuan ZN, Jin CJ, Wen LP, Zhang ZL, Xue Y, Yao XB. PhosSNP for Systematic Analysis of Genetic Polymorphisms That Influence Protein Phosphorylation. Molecular & Cellular Proteomics. 2010;9(4):623-634. (IF:4.828, cited by66)
- Ren J, Liu ZX, Gao XJ, Jin CJ, Ye ML, Zou HF, Wen LP, Zhang ZL, Xue Y, Yao XB. MiCroKit 3.0: an integrated database of midbody, centrosome and kinetochore. Nucleic Acids Research. 2010;38(D1):D155-D160. (IF:14.9, cited by 16)
- Jiang S, Xie YB, He ZH, Zhang Y, Zhao YL, Chen L, Zheng YY, Miao YY, Zuo ZX* and Ren J*. m6ASNP: a tool for annotating genetic variants by m6A function. GigaScience. 2018;7(5). (IF:4.688, cited by 7)
- Xie YB, Luo XT, Li YP, Chen L, Ma WB, Huang JJ, Cui J, Zhao Y, Xue Y, Zuo ZX* and Ren J*. DeepNitro: Prediction of Protein Nitration and Nitrosylation Sites by Deep Learning. Genomics, Proteomics & Bioinformatics. 2018;16(4): 294-306 (IF: 6.597, cited by 96)
- XieYB, Luo XT, LiHQ, Xu QX, He ZH, Zhao Q*, Zuo ZX*, Ren J*.autoRPA: A web server for constructing cancer staging models by recursive partitioning analysis. Computational and Structural Biotechnology Journal. 2020;18:3361-3367
- Li HY, Chen L, Huang ZL, Luo XT, Li HQ, Ren J*, Xie YB*. DeepOMe: A Web Server for the Prediction of 2′-O-Me Sites Based on the Hybrid CNN and BLSTM Architecture. Frontiers in Cell and Developmental Biology.2021;9:696894
- PengD, LiHQ, Hu BS, Zhang HW,Chen L,Lin SF,Zuo ZX,Yu Xue,Ren J*,XieYB*.PTMsnp: A Web Server for the Identification of Driver Mutations That Affect Protein Post-translational Modification. Frontiers in Cell and Developmental Biology. 2020;8:593661
- XieYB, Zheng YY, Li HY, Luo XT, He ZH, Cao S, Shi Y, Zhao Q, Xue Y, Zuo ZX, Ren J*. GPS-Lipid: a robust tool for the prediction of multiple lipid modification sites.Scientific Reports.2016;6:28249. (IF:4.122, cited by 150)
- Liu ZX, Cao J, Gao XJ, Zhou YH, Wen LP, Yang X, Yao XB, Ren J*, Xue Y*. CPLA 1.0: an integrated database of protein lysine acetylation. Nucleic Acids Research. 2011; 39(D1):D1029-1034. (IF:14.9, cited by 36)
- Xie SQ, Nie P, Wang Y, Wang H, Li H, Yang Z, Liu Y*, Ren J*, Xie Z*.RPFdb: a database for genome wide information of translated mRNA generated from ribosome profiling. Nucleic Acids Research. 2016;44(D1):D254-D258. (IF:14.9, cited by 27)
- Zhao Q, Sun Y, Liu ZK, Zhang HW, Li XY, Zhu KY, Liu ZX*, Ren J, Zuo ZX*. CrossICC: iterative consensus clustering of cross-platform gene expression data without adjusting batch effect. Briefings in Bioinformatics. 2019. 21(5):1-7(IF:9.101)
- Song CX, Ye ML, Jiang XN, Han GH, Songyang Z, Tan YX, Wang HY, Ren J*, Xue Y* & Zou HF*.Systematic analysis of protein phosphorylation networks from phosphoproteomic data. Molecular & Cellular Proteomics. 2012;11(10):1070-1083. (IF:4.828, cited by 87)
- Liu ZX#, Ren J#, Cao J#, HeJ, Yang Q, Ma Q, Gao XJ, Yao XB,Jin CJ, Xue Y.Systematic analysis of the Plk-mediated phosphoregulation in eukaryotes.Briefings in Bioinformatics. 2013;14 (3):344-360(IF:9.101, cited by 14)
- Chen L, Miao YY, Liu MN, Gao ZJ, Peng D, Zheng YY, Zuo ZX, Xie YB*, Ren J*. Pan-cancer analysis reveals the functional importance of protein lysine modification in cancer development. Frontiers in Genetics. 2018;9:254 (IF:3.517, cited by 4)
- Xue Y*, Gao XJ, Cao J, Liu ZX, Jin CJ, Wen LP, Yao XB, Ren J*. A Summary of Computational Resources for Protein Phosphorylation. Current Protein & Peptide Science. 2010;11(6):485-496. (IF:2.696, cited by 43)
- ZhengYY,GuoJJ, LiX, XieYB, HouMM, FuXY, DaiSK, DiaoRC, MiaoYY* and RenJ*. An integrated overview of spatiotemporal organization and regulation in mitosis in terms of the proteins in the functional supercomplexes.Frontiers in Microbiology. 2014;5:573(IF: 4.019, cited by 7)
- Xie YB, Luo XT, He ZH, Zheng YY, Zuo ZX, Zhao Q*, Miao YY* and Ren J*. VirusMap: A visualization database for the influenza A virus. Journal of Genetics and Genomics. 2017;44(4):281-284. (IF:4.066)
- Liu ZX, Gao X, Ma Q, Cao J, Ren J*, Xue Y*. GPS-CCD: A novel computational program for prediction of calpain cleavage sites. Plos One.2011;6(4):e19001. (IF:2.766, cited by 69)
- Liu ZX, Cao J, Ma Q, Gao XJ, Ren J*, Xue Y*. GPS-YNO2: computational prediction of tyrosine nitration sites in proteins. Mol Biosyst. 2011;7(4):1197-1204. (IF:2.759, cited by 57)
- Liu ZX, Ma Q, Cao J, Gao XJ, Ren J*, Xue Y*. GPS-PUP: computational prediction of pupylation sites in prokaryotic proteins. Mol Biosyst. 2011;7(10):2737-2740. (IF:2.759, cited by 32)
- Ren J, Gao XJ, Liu ZX, Cao J,Ma Q, Xue Y. Computational Analysis of Phosphoproteomics: Progresses and Perspectives. Current Protein & Peptide Science. 2011;7(12):591-601.(IF:2.696, cited by 11)



